Taq PCR Core Kit (1000 U)
Cat. No. / ID: 201225
特徴
- PCR条件の至適化が最小限で済むQIAGEN PCR Buffer
- 直接ゲルにロード可能なPCR バッファーでより迅速な操作
- GC リッチなテンプレートの増幅を促進するQ-Solution
- 簡便で取り扱いやすいフォーマット
製品詳細
パフォーマンス
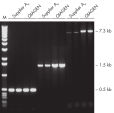
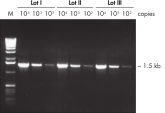
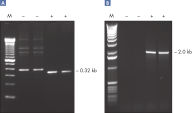
Taq PCR Core Kitは、他メーカーの試験されたキットに比べて優れており、時間のかかる至適化を必要とせずに、様々なPCRアプリケーションで確固たるPCR性能を示します。本キットには、スタンダードなPCRから特殊なPCRまで適応できる 高品質の組み換え酵素、Taq DNA Polymeraseが同梱されています(図 " Tm 値の異なるプライマーへの適応性" と" 長いPCR産物の特異的増幅")。TaqDNA Polymeraseは、全てのロットで、低コピー数のヒトゲノムDNAをターゲットとした増幅実験により、PCR特異性の厳密さや再現性をチェックするなど、広範囲な品質管理テストを受けています(図 " ロット間での再現性")。同様にキットに含まれているQIAGEN PCR BufferとCoralLoad PCR Bufferのユニークな組成によって、最小限の至適化要求事項と様々なPCR条件で、特異性の高いPCRが可能となります(図" 幅広い至適アニーリング温度"と " 異なったマグネシウム濃度への適応")。さらに、CoralLoad PCR Bufferは、PCR産物をアガロースゲルに即座にロードすることを可能にするため、比較的簡単な操作で比較的早く結果が得られます。また、キット付属のPCR 添加物、Q - Solutionを使用すれば、不適切なPCR条件を改善することができます(図 " 増幅困難なテンプレートの増幅")。
Taq DNAポリメラーゼの詳細データ
濃縮:5 units/µl
組み換え酵素:はい
基質類似体: dNTP、ddNTP、dUTP、ビオチン-11-dUTP、DIG-11-dUTP、蛍光-dNTP/ddNTP
エクステンション率72℃ で2~4 kb/分
半減期:97℃で10分、94℃で60分
増幅効率:≥105 倍
5'->3' エキソヌクレアーゼ活性:あり
余分なA付加:あり
3'->5' エキソヌクレアーゼ活性:なし
混入しているヌクレアーゼ:なし
混入しているRNase:なし
混入しているプロテアーゼ:なし
自己プライミング活性:なし
図参照
原理
Taq DNAポリメラーゼ
Taq DNAポリメラーゼ は、スタンダードなPCRから特殊なPCRまで適応できる 高品質の組み換え酵素です(図 " Tm 値の異なるプライマーへの適応性" と" 長いPCR産物の特異的増幅")。
QIAGEN PCR Buffer
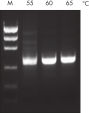
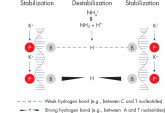
革新的なQIAGEN PCR Bufferは、PCR至適化の操作を軽減することにより、時間と労力を節約するために開発されました。QIAGEN PCR Bufferは、KCl も (NH4)2SO4 も含んでいます(図" プライマーのアニーリングにおける特異性が増加")。このユニークなバッファーによって、特異的PCRの産物を増幅しやすくなります。PCR サイクルごとのアニーリングの間、非特異的なプライマー結合に対する特異的な結合の比率が、バッファーによって高く保たれます。このPCRバッファーは、KClと (NH4)2SO4 のユニークな配合比により、従来のPCR バッファーに比べ幅広いアニーリング温度やMg2+濃度の範囲で厳密なプライマーアニーリング条件を実現します。異なるアニーリング温度あるいはMg2+ 濃度を用いて行なうPCRの至適化は、劇的に緩和され、多くの場合、不要となります(図 " 幅広い至適アニーリング温度"および" 異なったマグネシウム濃度への適応 ")。
CoralLoad PCR Buffer
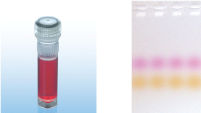
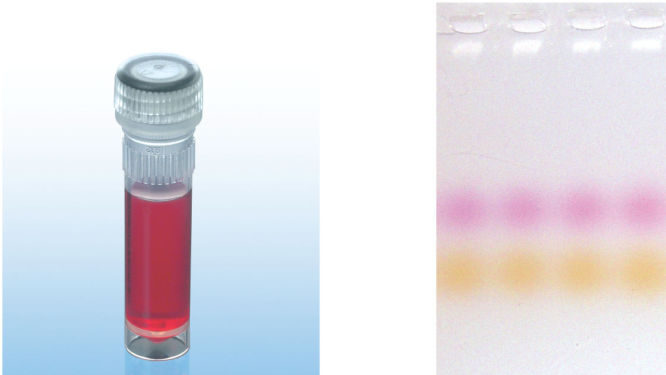
CoralLoad PCR Bufferは、QIAGEN PCR Bufferの全ての特長を持っています。さらに、PCR反応液をアガロースゲルに直接ロードするために使用することができ、従って、ゲルローディングバッファーを別途加える必要はありません。CoralLoad PCR Bufferは従来のQIAGEN PCR Bufferと同程度の高いPCR特異性を持ち、反応の至適化は最小限に抑えられます。さらに、これに入っている2種類のマーカー色素(オレンジ色の色素と赤色の色素)により、DNAの移動距離の予測とアガロースゲルの泳動時間の至適化を容易に行なえます(図" CoralLoad PCR Buffer")。本バッファーはピペッティングの目視化を改良し、PCR産物をゲルに直接ロードすることが可能なので、簡便性が増加します。
Q-Solution
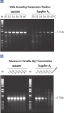
Q-Solution は、DNAの溶解挙動を変えることで、GCリッチなテンプレート、または二次構造が複雑なテンプレートを増幅しやすくします。この試薬の添加により、しばしば最適条件ではないPCRが改善されたり、今まで得られなかったPCR産物の増幅が可能になったりします (図 " 増幅困難なテンプレートをQ-Solutionにより増幅")。DMSO や他のPCR添加物と異なり、本溶液はどのようなプライマー/テンプレートシステムでも一定の濃度で作用し、毒性もありません。
図参照
操作手順
アプリケーション
Taq DNA Polymeraseは以下のようなスタンダードな用途にも特殊な用途にも使用できます。
- スタンダードな PCR
- RT-PCR
- スクリーニング
- PCRによるDNAフィンガープリンティング(VNTR、STR、RAPD)
裏付けデータと数値
CoralLoad PCR Buffer.
Specifications
| Features | Specifications |
|---|---|
| Applications | PCR, RT-PCR, DNA fingerprinting |
| Sample/target type | Genomic DNA and cDNA |
| Real-time or endpoint | Endpoint |
| dNTP's included | Yes |
| Single or multiplex | Single |
| Reaction type | PCR amplification |
| Mastermix | No |
| With/without hotstart | Without hotstart |
| Enzyme activity | 5' -> 3' exonuclease activity |