QuantiNova LNA PCR Assay (200)
Cat. No. / ID: 249990
Caractéristiques
- Plus de 1,3 million de dosages permettent la couverture la plus large et complète des transcrits d’ARNm et de lncARN dans Ensembl pour l’homme, la souris et le rat
- Sensibilité et spécificité exceptionnelles grâce à de courtes amorces améliorées par des LNA
- Détection exacte sur une large gamme dynamique à partir de 1 copie d’ARN
- Optimisés pour éliminer l’amplification non spécifique
- Quantification absolue des changements d’expression avec la dPCR à l’aide de l’instrument QIAcuity et du QIAcuity EG PCR Kit
Détails produit
Les QuantiNova LNA PCR Assays redéfinissent la norme dans l’analyse de l’expression génique reposant sur la PCR digitale. Choisissez parmi la plus large sélection de dosages préconçus pour la détection exacte et sensible de tout ARNm ou lncARN de l’homme, de la souris ou du rat – de la détection générale de transcrits à la différenciation d’isoformes de transcrits spécifiques. L’amélioration par des LNA nous permet de concevoir des amorces courtes qui présentent une plus grande flexibilité pour se positionner sur la cible. Par conséquent, nous pouvons optimiser la conception pour détecter un transcrit spécifique ou différencier des cibles. De plus, la validation complète de la conception garantit des performances optimales et une détection robuste. Pour la PCR digitale, nous avons optimisé les dosages avec les QIAcuity EG PCR Kits et l’instrument QIAcuity et créé une méthode de quantification absolue simple et rapide qui prend seulement 2 heures.
Avez-vous l’intention d’utiliser des QuantiNova LNA PCR Assays pour l’analyse par qPCR ? Vous trouverez des détails sur les produits spécifiques à la qPCR et sur leurs performances dans la page de catalogue consacrée à la qPCR.
Vous avez besoin d’un devis pour votre projet de recherche ou vous souhaitez discuter de votre projet avec notre équipe de spécialistes ? Il vous suffit de nous contacter !
Performances
Analyse de PCR digitale optimisée avec les QIAcuity EG PCR Kits et l’instrument QIAcuity
Les QuantiNova LNA PCR Assays ont été développés pour permettre une amplification des cibles avec une grande spécificité. Cela peut être quantifié par deux méthodes de PCR : la qPCR avec des thermocycleurs en temps réel classiques et la PCR digitale à l’aide de l’instrument QIAcuity et du QIAcuity EG PCR Kit (voir figure « Utilisation des QuantiNova LNA PCR Assays pour la PCR digitale »). Après la synthèse de l’ADNc à l’aide du QuantiTect Reverse Transcription Kit, la PCR digitale permet une quantification des cibles très précise, assurant la détection d’infimes changements d’expression aux concentrations les plus faibles. Un sous-ensemble des principaux dosages a été validé expérimentalement sur l’instrument QIAcuity.
Performances de la PCR améliorées par des LNA
Les QuantiNova LNA PCR Assays ont été développés à l’aide de critères de conception rigoureux et d’algorithmes validés en laboratoire. Le processus rigoureux de sélection des dosages garantit que chaque jeu d’amorces offre les plus grandes spécificité et efficacité pour l’obtention de résultats les plus fiables et exacts possible. La normalisation des Tm et l’amélioration par des LNA confèrent aux amorces une affinité de liaison plus élevée que les amorces d’ADN classiques, augmentant considérablement la sensibilité et la spécificité des dosages.
Cette sensibilité accrue garantit d’excellentes efficacités d’amplification à partir de 1 molécule d’ARN, simplifiant la détection des cibles en faible abondance telles que les lncARN avec de plus faibles quantités de matériel de départ. La spécificité augmentée par le positionnement judicieux des LNA vous fait bénéficier d’un plus grand rapport signal sur bruit, permettant la discrimination des séquences qui ne diffèrent que par un seul nucléotide et éliminant l’amplification non spécifique et la formation de dimères d’amorces.
Comme la haute affinité de liaison des bases des LNA augmente la flexibilité du placement des amorces sur le transcrit, nous sommes capables d’utiliser un positionnement judicieux afin de concevoir des dosages pour les cibles habituellement difficiles à analyser. Cela vous procure une meilleure discrimination des cibles et une quantification fiable, même pour les cibles riches en AU, les transcrits en faible abondance, les cibles avec une teneur élevée en structure secondaire et les échantillons très complexes.
Fiez-vous aux experts de la conception de LNA
Grâce à nos 20 ans d’expérience dans la conception de LNA, nous avons pu développer et optimiser notre algorithme de conception de LNA sophistiqué, qui intègre plus de 50 paramètres différents – tous complètement validés selon des critères de performances rigoureux –, afin d’assurer un dosage optimal pour détecter les cibles. Nous avons sélectionné jusqu’à trois conceptions différentes de dosages pour chaque transcrit et complètement validé en laboratoire humide tous les dosages d’ARNm et de lncARN courants. Les QuantiNova LNA PCR Assays fonctionnent, sans que vous ayez à consacrer du temps ni de l’argent à l’optimisation.
Principe
PCR digitale à base d’EvaGreen
Pour une quantification absolue par dPCR, utilisez les QuantiNova LNA PCR Assays avec le QIAcuity EG PCR Kit, qui fait appel une détection de fluorescence à base d’EvaGreen. EvaGreen est un colorant intercalant qui se fixe sur l’ADN double brin (comme SYBR® Green) et émet de la fluorescence après sa fixation sur l’ADN. L’utilisation de la dPCR à base d’EvaGreen offre commodité et économies, parce que vous n’avez besoin que du jeu d’amorces d’amplification et de détection du produit. Elle assure aussi une résolution plus élevée dans la réaction de dPCR, qui est divisée en milliers de partitions sur la nanoplaque de dPCR, de sorte que la concentration en amorces nécessaire pour la réaction de dPCR est moitié moindre que pour la qPCR.
La plus complète et la plus spécifique des couvertures
Notre algorithme exclusif a été utilisé pour concevoir plus de 1,3 million de QuantiNova LNA PCR Assays afin d’assurer l’analyse d’ARNm et de lncARN la plus sensible, exacte et efficace possible. Les dosages préconçus couvrent la plupart des transcrits dans la base de données Ensembl pour les gènes de l’homme, de la souris et du rat, permettant d’effectuer les études PCR de l’expression génique les plus approfondies possible. La plupart des dosages comportent un chevauchement d’intron et ne détectent que des ARN. Les dosages qui n’ont pas de chevauchement d’intron sont désignés comme tels, et s’il y a un exon dans la cible, les signaux non voulus peuvent être facilement éliminés à l’aide du QuantiTect Reverse Transcription Kit avec l’étape intégrée d’élimination de l’ADNg.
Choix du dosage adapté à votre cible
Les QuantiNova LNA PCR Assays préconçus vous permettent de détecter avec exactitude et sensibilité tout ARNm ou lncARN de l’homme, de la souris ou du rat, indépendamment du niveau d’analyse dont vous avez besoin : détection générale des transcrits, détection d’un transcrit spécifique ou différenciation entre des isoformes de transcrits.
La plupart des gènes de l’homme, de la souris et du rat n’ont qu’un seul transcrit, mais pour ceux qui ont plusieurs transcrits, nous avons sélectionné jusqu’à trois dosages par transcrit à l’aide du même algorithme. La conception et le positionnement des amorces de ces dosages diffèrent pour répondre à diverses exigences d’utilisation. Notre guide de sélection des dosages vous aide à identifier rapidement le meilleur dosage dans chaque catégorie. Après avoir recherché des dosages pour votre cible, examinez les résultats et cherchez le dosage recommandé correspondant à l’utilisation prévue :
- Meilleure couverture : pour la détection générale de transcrits
- Meilleur dosage de transcrits : pour la détection d’un transcrit spécifique
- Meilleur dosage spécifique à un transcrit : pour la différenciation entre des isoformes de transcrits spécifiques
Reportez-vous au tableau ci-dessous pour plus de détails.
| Dosages couvrant des gènes | Dosages spécifiques à un transcrit | ||
| Dosage recommandé par QIAGEN | Marqué « Meilleure couverture » | Marqué « Meilleur dosage de transcrits » | Marqué « Meilleur dosage spécifique à un transcrit » |
| Description de la conception et de la couverture du dosage | Couvre la plupart des transcrits biologiquement pertinents d’un gène donné |
Hautement optimisé pour détecter spécifiquement le transcrit d’intérêt, ciblant plus d’isoformes du transcrit |
Spécifique à un transcrit variant d’épissage |
| Quand choisir | Pour effectuer un criblage général de transcrits et déterminer si le gène d’intérêt est exprimé dans un échantillon ; pour détecter autant de transcrits et d’isoformes d’un gène que possible |
Pour détecter un transcrit spécifique | Pour différencier entre des isoformes spécifiques d’un transcrit |
Analyse des données de PCR digitale
La QIAcuity Software Suite est utilisée pour analyser les données de dPCR et comprend un test d’expression génique, qui donne les résultats sous forme d’ampleur du changement et d’ampleur de la régulation avec des figures prêtes pour la publication.
Reference Gene Assays pour n’importe quelle étude
Une large sélection de Reference Gene Assays, validés fonctionnellement pour l’homme, la souris et le rat, est disponible pour permettre une normalisation des données de haute qualité et assurer des résultats fiables. Ces dosages ciblent des ARN codants, de longs ARN non codants et de petits ARN nucléolaires endogènes qui sont généralement exprimés constitutivement dans une grande variété de tissus.
Normalisation des résultats de qPCR d’ARNm/lncARN
La normalisation élimine les variations techniques et biologiques entre les échantillons sans lien avec les changements biologiques étudiés. Il est essentiel d’effectuer une normalisation appropriée pour garantir une analyse et une interprétation correctes des résultats des expériences de real-time PCR. Le plus souvent, on utilise des gènes de référence exprimés de façon stable pour la normalisation.
Il est généralement recommandé de tester plusieurs gènes de référence de contrôle endogène avant de configurer votre analyse réelle d’expression des ARNm/lncARN. Ces gènes candidats doivent être choisis parmi des gènes qui doivent être exprimés de façon stable sur toute la gamme d’échantillons étudiés. Il peut s’agir d’ARNm ou de lncARN exprimés de façon stable sélectionnés en fonction de la littérature ou de données préexistantes (p. ex. criblage de panel de qPCR ou NGS). Le système QuantiNova LNA PCR comporte des dosages de gènes de référence validés pour les ARN qui ont tendance à être exprimés de façon stable et sont donc de bons candidats comme gènes de référence.
Tous les gènes candidats doivent être validés empiriquement pour chaque étude. Une façon de normaliser un panel de PCR lors du profilage d’un grand nombre d’ARNm/lncARN consiste à effectuer la normalisation par rapport à la moyenne globale – la moyenne de tous les ARNm/lncARN exprimés. Cette approche peut convenir aux échantillons à fort taux d’appel (gènes exprimés), mais elle doit être utilisée avec précaution pour les échantillons à faible taux d’appel. Cette approche n’est pas non plus appropriée pour les échantillons dans lesquels le niveau d’expression génique global est modifié.
Procédure
RT-dPCR en deux étapes
La réalisation de la réaction de transcription inverse à l’aide du QuantiTect Reverse Transcription Kit (réf. 205311, 205313, 205314) donne les meilleurs résultats. Il n’est pas recommandé d’utiliser le QuantiNova Reverse Transcription Kit. L’ADNc obtenu est ensuite quantifié par dPCR à l’aide des mélanges principaux du QIAcuity EG PCR Kit associé avec le QuantiNova LNA PCR Assay choisi.
Remarque importante : Les quantités réactionnelles indiquées entre parenthèses après les noms des produits de dosage sont destinées à une utilisation en qPCR. La PCR digitale ne requiert qu’une concentration moitié moindre en amorces, mais les volumes réactionnels sont différents. Avec la QIAcuity Nanoplate 26K, vous pouvez configurer les nombres de réactions indiqués ; avec la Nanoplate 8.5K vous pouvez en configurer 3,3 fois plus. Reportez-vous au manuel pour des instructions d’utilisation de QIAcuity en dPCR.
Expédition et livraison
Les QuantiNova LNA PCR Assays sont expédiés à température ambiante. Les dosages en stock sont livrés en 1–5 jours. Pendant la période d’accès anticipé, les délais de livraison peuvent être plus longs.
Ce dont vous avez besoin pour commencer la PCR digitale avec le système QuantiNova LNA PCR
Transcription inverse : QuantiTect Reverse Transcription Kit (réf. 205311, 205313, 205314)
Mélange principal de dPCR : QIAcuity EG PCR Kit
Dosages :
- QuantiNova LNA PCR Assays
- QuantiNova LNA PCR Custom Assays
Applications
Les QuantiNova LNA PCR Assays sont parfaitement adaptés aux applications telles que :
- L’analyse d’expression, le profilage et la quantification des ARNm et lncARN
- La validation des données d’expression génique RNA-seq
- Le profilage d’expression génique
- L’analyse des signaux et des voies
- La confirmation de l’inhibition de l’expression génique par des LNA GapmeRs ou des pARNi
- Le développement de biomarqueurs, y compris le criblage, l’identification et la validation de biomarqueurs associés à une maladie
- Le suivi des changements phénotypiques en lien avec l’expression génique
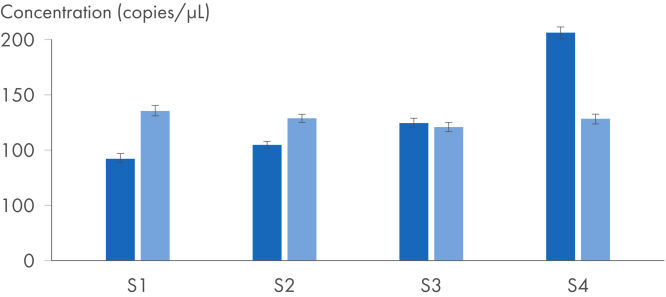
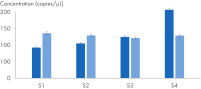
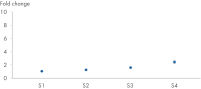
Données et illustrations utiles
Analyse de l’expression du gène IL-4 – détection de faibles changements d’expression avec la plus grande précision.