✓ Automatische Verarbeitung von Online-Bestellungen 24/7
✓ Sachkundiger und professioneller technischer und Produkt-Support
✓ Schnelle und zuverlässige (Nach-)Bestellung
QIAquick PCR Purification Kit (50)
Cat. No. / ID: 28104
✓ Automatische Verarbeitung von Online-Bestellungen 24/7
✓ Sachkundiger und professioneller technischer und Produkt-Support
✓ Schnelle und zuverlässige (Nach-)Bestellung
Eigenschaften
- Rückgewinnung von gebrauchsfertiger DNA von bis zu 95 %
- Reinigung von DNA von bis zu 10 kb Länge in drei einfachen Schritten
- Gel-Ladefarbstoff für komfortable Probenanalyse
- Kombikit zur Gelextraktion und PCR-Reinigung
- Spin-Säulen separat erhältlich
Angaben zum Produkt
Das QIAquick PCR Purification Kit enthält Spin-Säulen, Puffer und Sammelröhrchen für die Silikamembran-basierte Aufreinigung von PCR-Produkten > 100 bp. DNA von bis zu 10 kb wird durch einfaches und schnelles Verfahren mit den Schritten „Binden-Waschen-Eluieren“ mit einem Elutionsvolumen von 30–50 μl aufgereinigt. Ein optionaler pH-Indikator ermöglicht die einfache Bestimmung des optimalen pH-Werts für die DNA-Bindung an die Spin-Säule. Das Verfahren kann auf dem QIAcube Connect vollständig automatisiert werden.
Für optimale Ergebnisse wird empfohlen, dieses Produkt zusammen mit QIAvac 24 Plus zu verwenden.
Die Standardprotokolle für die QIAquick PCR-Aufreinigung können auch mit dem TRACKMAN Connected System in Verbindung mit PIPETMAN M Connected Pipetten, beide von Gilson, durchgeführt werden. Das TRACKMAN Connected System führt durch die Protokolle für die QIAquick PCR-Aufreinigung und passt die Einstellungen der Bluetooth-fähigen PIPETMAN M Connected Pipette automatisch an. Jeder Schritt der Protokollausführung wird aufgezeichnet, um die Berichterstattung mithilfe eines umfassenden Laufberichts zu beschleunigen. Weitere Informationen herunterladen.
Leistung
Abbildungen ansehen
Prinzip
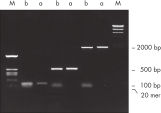
QIAquick Kits enthalten eine Silika-Membraneinheit für die Bindung von DNA in Hochsalzpuffer und die Elution mit Niedrigsalzpuffer oder Wasser. Durch die Aufreinigung werden Primer, Nukleotide, Enzyme, Mineralöl, Salze, Agarose, Ethidiumbromid und andere Verunreinigungen aus DNA-Proben entfernt (siehe Abbildung „ Vollständige Primerentfernung nach PCR“). Die Silika-Membrantechnologie beseitigt die Probleme und Schwierigkeiten, die mit losen Harzen und Suspensionen verbunden sind. Spezialisierte Bindepuffer sind für spezifische Anwendungen optimiert und fördern die selektive Adsorption von DNA-Molekülen innerhalb bestimmter Größenbereiche.
Gel-Ladefarbstoff
Der mitgelieferte Gel-Ladefarbstoff ermöglicht eine schnellere und bequemere Verarbeitung und Analyse der Proben. Der GelPilot Loading Dye enthält drei Farbstoffe zur Nachverfolgung (Xylencyanol, Bromphenolblau und Orange G), um die Optimierung der Agarosegel-Laufzeit zu erleichtern und zu verhindern, dass kleinere DNA-Fragmente zu weit migrieren (siehe Abbildung „ GelPilot Loading Dye“).
Abbildungen ansehen
Verfahren
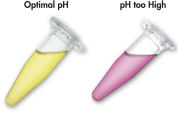
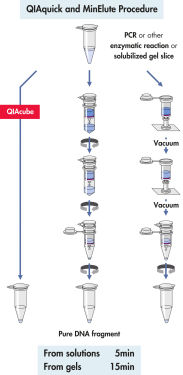
Das QIAquick System nutzt ein einfaches Verfahren mit den Schritten „Binden-Waschen-Eluieren“ (siehe Flussdiagramm „ QIAquick- und MinElute-Verfahren“). Der Bindepuffer wird direkt zur PCR-Probe oder einer anderen enzymatischen Reaktion hinzugefügt und die Mischung wird auf die QIAquick Spin Column aufgetragen. Zur einfachen Bestimmung des optimalen pH-Werts für die DNA-Bindung enthält der Bindepuffer einen pH-Indikator (siehe Abbildung „pH-Indikatorfarbstoff“). Die Nukleinsäuren werden unter den Hochsalzbedingungen des Puffers an die Silikamembran adsorbiert. Verunreinigungen werden durch Waschen entfernt, und die reine DNA wird in einem kleinen Volumen des mitgelieferten Niedrigsalzpuffers oder mit Wasser eluiert und kann direkt für alle nachfolgenden Anwendungen genutzt werden.
Handhabung
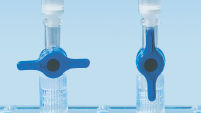
QIAquick Spin Columns sind so konzipiert, dass sie zwei praktische Optionen für die Handhabung bieten. Die Spin-Säulen passen in eine herkömmliche Tisch-Mikrozentrifuge oder auf jeden Vakuumverteiler mit Luer-Anschlüssen, beispielsweise QIAvac 24 Plus mit QIAvac Luer Adapters. Das QIAquick PCR Purification Kit sowie andere QIAGEN Kits auf Spin-Säulen-Basis können auf dem QIAcube vollständig automatisiert werden, was eine höhere Produktivität und die Standardisierung der Ergebnisse ermöglicht (siehe Abbildungen „Handhabungsoptionen für Spin-Säulen A, B, C und D“ und „ QIAcube Connect“).
Abbildungen ansehen
Anwendungen
Die mit dem QIAquick System aufgereinigten DNA-Fragmente können direkt für alle Anwendungen verwendet werden, darunter Sequenzierung, Microarray-Analyse, Ligation und Transformation, Restriktionsverdau, Markierung, Mikroinjektion, PCR und In-vitro-Transkription.
Ergänzende Daten und Abbildungen
QIAquick- und MinElute-Verfahren
Specifications
| Features | Specifications |
|---|---|
| Binding capacity | 10 µg |
| Technology | Silika-Technologie |
| Sample type: applications | ssDNA oder dsDNA aus PCR und anderen enzymatischen Reaktionen |
| Fragments removed | < 40mere |
| Elution volume | > 30 µl |
| Fragment size | 100 bp – 10 kb |
| Processing | Manuell |
| Format | Röhrchen |
| Type(s) of DNA recovered | ssDNA und dsDNA |